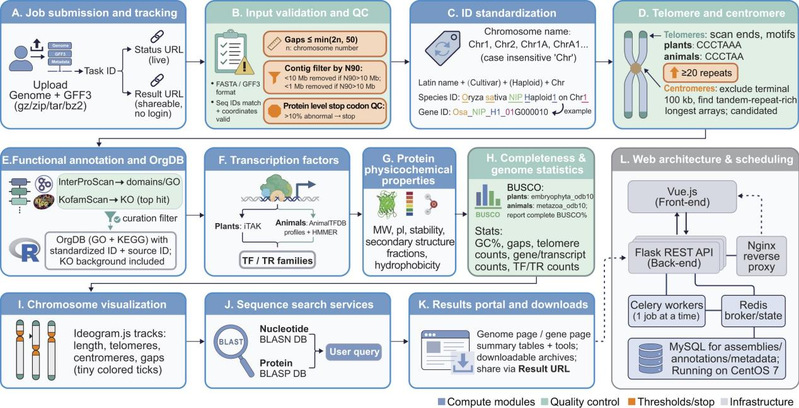
近年来,随着第三代测序技术的发展,端粒到端粒(Telomere-to-telomere,T2T)基因组组装逐渐成为生命科学研究的前沿方向。完整无缺口的基因组不仅有助于解析复杂基因组区域,还为物种进化、功能基因研究和精准育种提供了关键基础。然而,目前针对T2T基因组的分析工具仍较为分散,缺乏统一、高效且易用的平台。
5月6日,生命科学学院陈铭团队在Nucleic Acids Research在线发表题为“T2T-Hub:a central platform for analyzing plant and animal telomere-to-telomere genomes”的研究论文。该研究开发了T2T-Hub,一个面向动植物T2T基因组的综合分析与可视化平台。该平台集成了标准化分析流程、功能注释体系以及交互式可视化模块,致力于为完整基因组研究提供统一、高效的解决方案。目前,T2T-Hub已基于统一流程系统性整合并分析了230个植物和39个动物高质量T2T基因组,构建了跨物种可比的参考框架。用户只需上传基因组序列(FASTA)及注释文件(GFF3),即可自动完成从数据校验、质量评估到功能注释的一整套分析流程,无需编程基础即可开展复杂的基因组研究。

T2T-Hub支持多种核心分析任务,包括基因组完整性评估(BUSCO)、端粒与着丝粒识别、转录因子预测、GO/KEGG功能注释以及蛋白理化性质分析。同时,T2T-Hub提供交互式基因组浏览(如JBrowse2)、染色体结构可视化(Ideogram)及序列比对(BLAST)等功能,使研究人员能够在同一平台内完成从数据分析到结果探索的全过程。此外,平台还集成了比较基因组学工具(如共线性分析与系统发育分析),并支持同源基因识别、基因表达模式探索及多种在线分析工具(引物设计、序列检索等)。所有结果均可通过可分享的永久链接访问,大幅提升科研协作效率。整体而言,T2T-Hub通过“分析+注释+可视化+共享”的一体化设计,显著降低了T2T基因组研究的技术门槛,推动完整基因组时代的功能与进化研究。
浙江大学生命科学学院、“农学+X”多学科交叉人才培养中心博士研究生晁好瑜、南京大学生命科学学院硕士研究生阮忠豪和李卓瑾为本文的共同第一作者。浙江大学生命科学学院冯聪博士后、南京大学生命科学学院陈迪俊副教授和浙江大学生命科学学院陈铭教授为本文共同通讯作者。该工作同时受浙江大学农业与生物技术学院沈星星教授的帮助。研究得到国家自然科学基金委面上项目、国家自然科学基金国际合作项目、国家重点研发计划政府间国际科技创新合作重点专项的资助与支持。



